Nucleosoma para niños
El nucleosoma es como una pequeña bobina que ayuda a organizar las largas hebras de ADN dentro de las células de los seres vivos, especialmente en aquellas que tienen un núcleo (llamadas células eucariotas). Imagina tu ADN como un hilo muy largo; el nucleosoma lo enrolla de forma ordenada para que quepa dentro de los cromosomas de la célula.
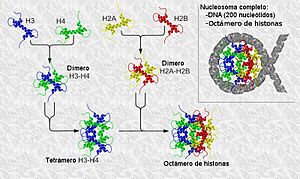
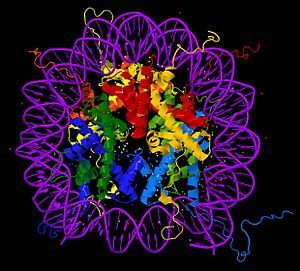
Cada nucleosoma está hecho de aproximadamente 145-150 pares de bases de ADN que se enrollan alrededor de un grupo de ocho proteínas especiales llamadas histonas. Este grupo de ocho proteínas se conoce como octámero. Cada octámero de histonas está formado por dos copias de cada una de las proteínas H2A, H2B, H3 y H4. La histona H1 es diferente, ya que se une por fuera del nucleosoma.
Los nucleosomas se organizan como si fueran las cuentas de un collar. Estas "cuentas" se pliegan una y otra vez para formar un cromosoma completo. Cada célula humana tiene alrededor de 30 millones de nucleosomas. Las histonas son proteínas muy importantes y se han mantenido casi iguales a lo largo de la evolución de las especies.
Nucleosoma: El Empaquetador del ADN
¿Cómo se descubrieron los nucleosomas?
En 1974, los científicos Don y Ada Ollins fueron los primeros en ver los nucleosomas. Usaron un microscopio electrónico y los observaron como pequeñas partículas redondas en la cromatina. Ese mismo año, Roger Kornberg los identificó y propuso cómo estaban hechos, basándose en varias pistas:
Primeras observaciones y pistas
- La cromatina tiene casi la misma cantidad de histonas H2A, H2B, H3 y H4, y menos de la mitad de H1.
- La histona H1 se encuentra fuera de la parte central del nucleosoma. Se une al ADN espaciador, que es el ADN que conecta un nucleosoma con el siguiente.
- Estudios con rayos X mostraron que la cromatina tiene una estructura que se repite regularmente. Este mismo patrón se veía cuando se mezclaba ADN puro con histonas (excepto la H1).
- Imágenes de microscopía electrónica de la cromatina revelaron que parecía un "collar de cuentas". Las cuentas eran las partículas de nucleosomas, y el hilo era el ADN.
- Al cortar la cromatina con una enzima especial (nucleasa de micrococo), se obtenían fragmentos de ADN que siempre eran múltiplos de unas 200 pares de bases. Esto se comprobó con una técnica llamada electroforesis en gel.
- Experimentos mostraron que las histonas H3 y H4 se unen para formar un grupo de cuatro (un tetrámero).
El modelo de Kornberg
Las observaciones de Kornberg lo llevaron a pensar que el nucleosoma está formado por un octámero (un grupo de ocho histonas: dos de H2A, dos de H2B, dos de H3 y dos de H4) y unas 200 pares de bases de ADN. De ese ADN, entre 140 y 147 pares de bases están en contacto directo con el centro del octámero. El ADN que conecta dos nucleosomas (el ADN espaciador) mide entre 20 y 100 pares de bases. Kornberg sugirió que la quinta histona, la H1, se unía de alguna manera por fuera del nucleosoma.
Cuando el ADN se copia dentro de la célula, las nuevas hebras de ADN se unen rápidamente a los nucleosomas.
Más tarde, en 1987, otros investigadores demostraron que los nucleosomas ayudan a controlar cuándo se "lee" el ADN (un proceso llamado transcripción).
¿Cómo es la estructura de un nucleosoma?
La parte central del nucleosoma
La parte central del nucleosoma tiene una sección de ADN de 140-147 nucleótidos de largo. Este ADN se enrolla alrededor del octámero de histonas dando 1.7 vueltas. El octámero está formado por las histonas H2A, H2B, H3 y H4, cada una en parejas. Entre cada nucleosoma hay un trozo de ADN llamado ADN espaciador, que puede medir entre 20 y 100 nucleótidos, dependiendo de la especie y el tipo de célula. Toda esta estructura forma una especie de hélice.
Estas partículas se pueden ver con un microscopio electrónico. Cuando la cromatina se "desenrolla" un poco, se ve como un "collar de cuentas". El hilo del collar es el ADN, y las cuentas son los nucleosomas. Si se corta el ADN que no está unido a los nucleosomas, se obtienen fragmentos que son múltiplos de unas 200 nucleótidos. Esto se puede ver con la técnica de electroforesis en gel. Este tipo de corte del ADN también puede ocurrir de forma natural cuando las células mueren de forma programada (un proceso llamado apoptosis).
Las "colas" de las histonas
Las histonas tienen unas "colas" en sus extremos que son muy flexibles y no tienen una forma definida. Se cree que estas colas son importantes para cómo se organizan los nucleosomas. Por ejemplo, la cola de la histona H4 puede interactuar con otras partes de los nucleosomas vecinos, lo que podría influir en cómo se empaqueta la cromatina.
La cromatina: ADN bien organizado
La repetición de los nucleosomas, junto con la histona H1 y el ADN espaciador, forma una fibra más compacta de 30 nanómetros. Esta fibra reduce la longitud del ADN hasta 50 veces. Para que el ADN pueda ser "leído" (proceso llamado transcripción), debe separarse de las histonas. Cuando el ADN está más "desplegado" y accesible, se le llama Eucromatina. Se cree que la eucromatina es la forma de 11 nanómetros, y la heterocromatina es la forma más compacta de 30 nanómetros.
Galería de imágenes
¿Cómo se forman los nucleosomas en la célula?
El papel de las histonas H3 y H4
Cuando el ADN se copia, las histonas H3 y H4 de los nucleosomas "viejos" se quedan cerca del ADN. Un grupo de proteínas llamado CAF-1 ayuda a ensamblarlas. Las histonas H3 y H4 que se acaban de fabricar son ensambladas por otro grupo llamado RCAF. Las histonas "viejas" mantienen sus modificaciones químicas, lo que ayuda a pasar información importante a las nuevas células. Las histonas recién hechas se modifican gradualmente a medida que la cromatina madura.
El papel de las histonas H2A y H2B
A diferencia de las histonas H3 y H4, las histonas H2A y H2B "viejas" se eliminan. Por eso, se usan histonas H2A y H2B recién fabricadas para los nuevos nucleosomas. Estas se unen en parejas y se incorporan al nucleosoma gracias a una proteína llamada NAP-1. También intervienen otros grupos de proteínas que ayudan a organizar los nucleosomas en estructuras más grandes.
¿Se pueden crear nucleosomas en el laboratorio?
Es posible crear nucleosomas en el laboratorio. Esto se puede hacer usando histonas purificadas o histonas creadas artificialmente.
Cómo se forman en el laboratorio
Una forma común de hacer que el ADN se enrolle alrededor de las histonas es usando una técnica con diferentes concentraciones de sal. Se mezclan secuencias de ADN y los octámeros de histonas en una solución con mucha sal. Luego, se reduce la concentración de sal poco a poco. A medida que la sal disminuye, el ADN se enrolla alrededor de los octámeros de histonas, formando los nucleosomas.
Haciéndolos más estables
También es posible hacer que los nucleosomas sean más estables en el laboratorio. Esto se logra creando "puentes" especiales entre las histonas o entre las histonas y el ADN. Por ejemplo, se pueden unir las dos copias de la histona H2A para que el octámero sea más fuerte. También se puede crear un puente entre la histona H3 y el ADN, lo que hace que la parte central del nucleosoma sea más resistente.
Véase también
 En inglés: Nucleosome Facts for Kids
En inglés: Nucleosome Facts for Kids